 注册
登录
注册
登录
 注册
登录
注册
登录
关于拉氏图的更多介绍,可以参考下这篇博客,这里简单引述一部分内容:
Ramachandran plot(拉氏图)是由G. N. Ramachandran等人于1963年开发的,用来描述蛋白质结构中氨基酸残基二面角\(\psi\)和\(\phi\)是否在合理区域的一种可视化方法。同时也可以反映出该蛋白质的构象是否合理。
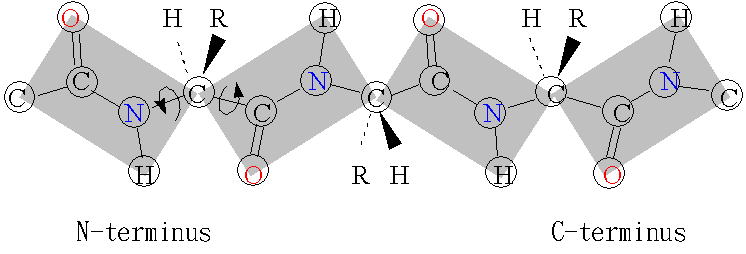
思路是比较简单的,就是找到一个蛋白质主链中的C,C\(_{\alpha}\),N,O这几种原子,然后计算对应共价键的二面角即可。计算相关内容可以参考我之前写过的这两篇文章:AlphaFold2中的残基刚体表示
和使用numpy计算分子内坐标。这里我们就简单的做一个Python的脚本,可以用来读取pdb文件,生成对应的拉氏图,用来判断对应的蛋白质构象是否合理,也可以用来比较两个同类蛋白之间的构型差异。
先把下面这个Python脚本文件保存到本地为rplot.py:
# rplot.py
"""
README
Run this script with command:
```bash
$ python3 rplot.py --input ../tutorials/pdb/case5.pdb --levels 8 --sigma 0.2 --grids 30
```
Requirements
hadder, numpy, matplotlib
"""
try:
from hadder.parsers import read_pdb
except ImportError:
import os
os.system('python3 -m pip install hadder --upgrade')
from hadder.parsers import read_pdb
import matplotlib.pyplot as plt
import numpy as np
import argparse
parser = argparse.ArgumentParser()
parser.add_argument("--input", help="Set the input pdb filename. Absolute file path is recommended.")
parser.add_argument("--levels", help="Contour levels.", default='8')
parser.add_argument("--sigma", help="KDE band width.", default='0.2')
parser.add_argument("--grids", help="Number of grids.", default='30')
args = parser.parse_args()
pdb_name = args.input
num_levels = int(args.levels)
sigma = float(args.sigma)
num_grids = int(args.grids)
def plot(fig, X, Y, Z, num_levels=8):
plt.xlabel(r'$\psi$')
plt.ylabel(r'$\phi$')
levels = np.linspace(np.min(Z), np.max(Z), num_levels)
fc = plt.contourf(X, Y, Z, cmap='Greens', levels=levels)
plt.colorbar(fc)
return fig
def torsion(crds, index1, index2, index3, index4):
crd1 = crds[index1]
crd2 = crds[index2]
crd3 = crds[index3]
crd4 = crds[index4]
vector1 = crd1 - crd2
vector2 = crd4 - crd3
axis_vector = crd3 - crd2
vec_a = np.cross(vector1, axis_vector)
vec_b = np.cross(vector2, axis_vector)
cross_ab = np.cross(vec_a, vec_b)
axis_vector /= np.linalg.norm(axis_vector, axis=-1, keepdims=True)
sin_phi = np.sum(axis_vector * cross_ab, axis=-1)
cos_phi = np.sum(vec_a * vec_b, axis=-1)
phi = np.arctan(sin_phi / cos_phi)
return phi
def psi_phi_from_pdb(pdb_name):
pdb_obj = read_pdb(pdb_name)
atom_names = pdb_obj.flatten_atoms
crds = pdb_obj.flatten_crds
c_index = np.where(atom_names=='C')[0]
n_index = np.where(atom_names=='N')[0]
ca_index = np.where(atom_names=='CA')[0]
psi = torsion(crds, n_index[:-1], ca_index[:-1], c_index[:-1], n_index[1:])
phi = torsion(crds, c_index[:-1], n_index[1:], ca_index[1:], c_index[1:])
return psi, phi
def gaussian2(x1, x2, sigma1=1.0, sigma2=1.0, A=0.5):
return np.sum(A*np.exp(-0.5*(x1**2/sigma1**2+x2**2/sigma2**2))/np.pi/sigma1/sigma2, axis=-1)
def potential_energy(position, psi, phi, sigma1, sigma2):
# (A, )
psi_, phi_ = position[:, 0], position[:, 1]
# (A, R)
delta_psi = psi_[:, None] - psi[None]
delta_phi = phi_[:, None] - phi[None]
# (A, )
Z = -np.log(gaussian2(delta_psi, delta_phi, sigma1=sigma1, sigma2=sigma2, A=2.0)+1)
return Z
psi_grids = np.linspace(-np.pi, np.pi, num_grids)
phi_grids = np.linspace(-np.pi, np.pi, num_grids)
grids = np.array(np.meshgrid(psi_grids, phi_grids)).T.reshape((-1, 2))
psi, phi = psi_phi_from_pdb(pdb_name)
Z = potential_energy(grids, psi, phi, sigma, sigma).reshape((psi_grids.shape[0], phi_grids.shape[0])).T
X,Y = np.meshgrid(psi_grids, phi_grids)
fig = plt.figure()
plt.title('Ramachandran plot for {}'.format(pdb_name.split('/')[-1]))
plot(fig, X, Y, Z, num_levels=num_levels)
plt.plot(psi, phi, '.', color='black')
plt.show()
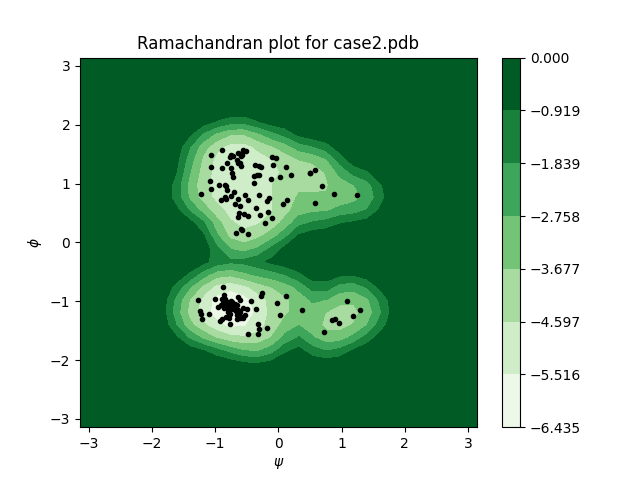
然后加载一个本地pdb文件:
$ python rplot.py case2.pdb
生成图像效果如下:
关于这个脚本还有一些常量可以配置:
$ python3 rplot.py --help
usage: rplot.py [-h] [--input INPUT] [--levels LEVELS] [--sigma SIGMA]
[--grids GRIDS]
optional arguments:
-h, --help show this help message and exit
--input INPUT Set the input pdb filename. Absolute file path is
recommended.
--levels LEVELS Contour levels.
--sigma SIGMA KDE band width.
--grids GRIDS Number of grids.
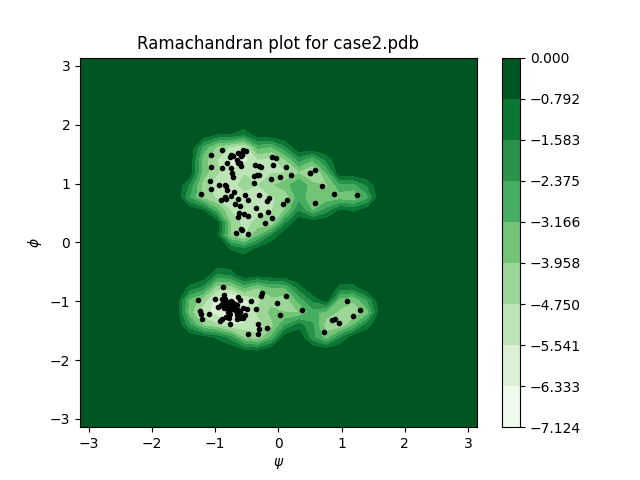
例如说,我们可以把KDE中高斯波包的sigma值配置的更小一点(默认值为0.2),这样图像显示的会更集中,还可以把levels调多一点(默认值为8),这样显示的等高线会更密一些:
$ python3 rplot.py --input ../tutorials/pdb/case2.pdb --sigma 0.1 --levels 10
效果如下:
这里我提供了一个用于画拉氏图的Python脚本源代码,供大家免费使用。虽然现在也有很多免费的平台和工具可以用,但很多都是黑箱,有需要的开发者可以直接在这个脚本基础上二次开发,定制自己的拉氏图绘制方法。
本文首发链接为:https://www.cnblogs.com/dechinphy/p/rplot.html
作者ID:DechinPhy
更多原著文章:https://www.cnblogs.com/dechinphy/
请博主喝咖啡:https://www.cnblogs.com/dechinphy/gallery/image/379634.html